Page 35 - 《广西植物》2026年第1期
P. 35
1 期 韦伶芝等: 凹脉金花茶的遗传多样性和群体遗传结构分析 3 1
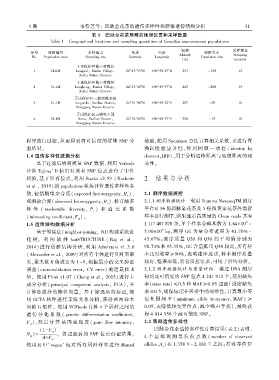
表 1 凹脉金花茶居群的地理位置和采样数量
Table 1 Geographical locations and sampling quantities of Camellia impressinervis populations
海拔 采样数量
序号 居群编号 采样地点 纬度 经度 居群大小
Altitude Sampling
No. Population code Sampling site Latitude Longitude Population size
(m) quantity
下雷保护区板六村陇位
1 CI ̄LW Longweiꎬ Banliu Villageꎬ 22°43′33″N 106°50′47″E 251 ~ 150 15
Xialei Nature Reserve
下雷保护区板六村陇恒
2 CI ̄LH Longhengꎬ Banliu Villageꎬ 22°43′48″N 106°49′57″E 245 ~ 200 15
Xialei Nature Reserve
弄岗保护区三联站陇米督
3 CI ̄LM Longmiduꎬ Sanlian Stationꎬ 22°31′08″N 106°50′22″E 257 ~ 50 16
Nonggang Nature Reserve
弄岗保护区三联站卜那
4 CI ̄BN Bunaꎬ Sanlian Stationꎬ 22°32′50″N 106°48′37″E 358 ~ 15 10
Nonggang Nature Reserve
程序进行过滤ꎬ从而得到高可信度的群体 SNP 分 检验ꎬ使用 Spearman 方法计算相关系数ꎬ并进行置
型结果ꎮ 换以检 验 显 著 性ꎬ 得 到 同 源 一 致 性 ( identity by
1.4 遗传多样性数据分析 descentꎬIBD)ꎬ用于分析遗传距离与地理距离的相
基于过滤后的高质量 SNP 数据ꎬ利用 Vcftools 关性ꎮ
计算 Tajima’ D 值且对所有 SNP 位点进行了中性
2 结果与分析
检验ꎬ基于所有位点ꎬ利用 Stacks v2.59 ( Rochette
et al.ꎬ 2019)的 populations 模块计算遗传多样性参
数ꎬ包括期望杂合度( expected heterozygosityꎬH )、 2.1 测序数据质控
e
观测杂合度(observed heterozygosityꎬH )、核苷酸多 2.1.1 测序数据统计 利用 Illumina NovaseqTM 测序
o
样 性 ( nucleotide diversityꎬ P ) 和 近 交 系 数 平台对 56 份凹脉金花茶及 3 份淡黄金花茶外类群
i
(inbreeding coefficientꎬF )ꎮ 样本进行测序ꎬ结果显示高质量的 Clean reads 共有
is
1.5 遗传结构数据分析 1 117 487 878 条ꎬ单个样本总碱基数为 1.64×10 ~
9
9
基于邻接法(neighbor ̄joiningꎬ NJ)构建系统进 5.90×10 bpꎬ测序 GC 含量分布范围为 41.70% ~
45.67%ꎻ测序质 量 Q20 和 Q30 的 平 均 值 分 别 为
化 树ꎮ 利 用 软 件 fastSTRUCTURE ( Raj et al.ꎬ
2014)进行居群结构分析ꎬ利用 Admixture v1.3.0 98.74%和 95.35%ꎬGC 含量低且 Q30 较高ꎬ所有样
(Alexander et al.ꎬ 2009)对所有个体进行贝叶斯聚 本比对效率≥90%ꎬ表明建库成功ꎬ样本测序质量
类ꎬ聚类数 K 值设置为 1 ~ 9ꎬ根据最小的交叉验证 较好ꎬ错误率低ꎬ符合质控要求ꎬ可用于后续分析ꎮ
误差( cross ̄validation errorꎬ CV error) 确定最佳 K 2.1.2 测序数据统计与质量评估 通过 DNA 测序
值ꎮ 使用 Plink v1.07 (Chang et al.ꎬ 2015) 进行主 得到高可信度的 SNP 位点 4 241 912 个ꎬ使用缺失
成分分析( principal component analysisꎬ PCA)ꎬ并 率(miss rate)≤0.5 和 MAF≥0.05 过滤[设定缺失
计算各成分的特征向量ꎮ 基于筛选后的标记ꎬ使 率≤0.5ꎬ确保标记在居群中的完整性ꎬ计算最小等
用 GCTA 软件进行亲缘关系分析ꎬ获得两两样本 位基 因 频 率 ( minimum allele frequencyꎬ MAF) ≥
间的 G 矩阵ꎮ 使用 VCFtools 计算 4 个居群之间的 0.05ꎬ去除低频变异位点ꎬ减少噪声干扰]ꎬ最终获
遗 传 分 化 系 数 ( genetic differentiation coefficientꎬ 得 4 014 956 个高可信度 SNPꎮ
F )ꎬ然 后 计 算 基 因 流 强 度 ( gene flow intensityꎬ 2.2 居群遗传多样性
st
(1-F ) 凹脉金花茶遗传多样性计算结果(表 2)表明ꎬ
st
N )= ꎮ 将过滤后的 SNP 位点标记结果ꎬ
m 4×F 4 个 居 群 观 测 等 位 位 点 数 ( number of observed
st
allelesꎬA )在 1.358 9 ~ 2.181 7 之间ꎻ有效等位位
使用 R 中‘ vegan’ 包对所有居群样本进行 Mantel o